On parle de transcriptomique lorsqu’on étudie les ARN, c’est à dire l’étape intermédiaire entre l’ADN et les protéines. Cependant, il existe aussi des ARN non codants, qui ne donnent pas de protéines, et dont les rôles sont toujours en cours d’étude. La totalité des ARN forme ce qu’on appelle le transcriptome. La transcriptomique est un champ très large qui va permettre l’analyse des mécanismes de transcription, de la régulation de ces phénomènes et des interactions entre ARN, protéines et autres facteurs.
Comment étudie-t-on le transcriptome ?
Tout comme l’étude de l’ADN, l’analyse des ARN regroupe des techniques de séquençage. On retrouve notamment les techniques de séquençage précédé d’une retro-transcription (afin de lire la séquence ADN), aussi appelée RNA-Seq [1] et les techniques de microarray [2] (comme les puces à ADN mais pour l’ARN). Ces techniques sont très similaires à celles utilisées pour l’ADN (voir dossier génomique) et donnent, au delà d’une information de séquence utile pour dépister des mutations ou des erreurs de transcription, une information quantitative, permettant de déterminer à quel niveau un ARN est exprimé. On parlera alors de taux d’expression d’un ARN donné : lorsque ce taux est élevé, l’ADN va transcrire plusieurs copies d’ARN, permettant une expression importante de protéines. A l’inverse, lorsque ce taux est bas, l’ADN va être peu ou pas transcrit, donnant lieu à peu de protéines par la suite. Ces taux d’expression peuvent varier avec le temps et/ou les pathologies. Plusieurs sites répertorient les analyses transcriptomiques dans le but de réunir tous les transcriptomes en fonction des organes, des pathologies, de l’âge, d’un traitement ou encore de l’exposition à des facteurs externes; vous pouvez allez visiter ce site (en anglais) ou ce site (en anglais) par exemple.
La PCR quantitative comme outil de transcriptomique
La PCR quantitative, ou PCR en temps réel, est une technique relativement dédiée à l’étude du transcriptome. Bien que plus fastidieuse que les approches RNAseq ou les microarrays, elle reste l’approche de choix pour l’étude de l’ARN du fait de son faible coût [3].
PCR veut dire « polymerase chain reaction » ou réaction en chaîne par polymérase. Ce nom barbare signifie simplement que la technique est basée sur l’action d’une enzyme spécifique, la polymérase, qui va permettre la synthèse d’un brin complémentaire d’ADN.
Étant donné que ce qui nous intéresse, c’est l’ARN, il va falloir rétro-transcrire l’ARN en ADN. Après cette rétro-transcription, on obtient un ADN sans régions non codantes, correspondant au gène. Une fois cet ADN obtenu, la PCR permet de suivre la synthèse de son brin complémentaire grâce à des marqueurs (généralement des fluorochromes). Plus il y a d’ARN à la base, plus il y aura d’ADN rétro-transcrit et plus le nombre de brins complémentaires va augmenter rapidement, donnant ainsi une information quantitative sur l’ARN d’intérêt. En général, on réalise 40 cycles dits « d’amplification » (c’est à dire correspondant à un cycle de synthèse des brins complémentaires). A un moment donné, le signal émis par les brins complémentaires va passer au-dessus d’une certaine limite, donnant une valeur qu’on appelle Ct (pour « cycle threshold).
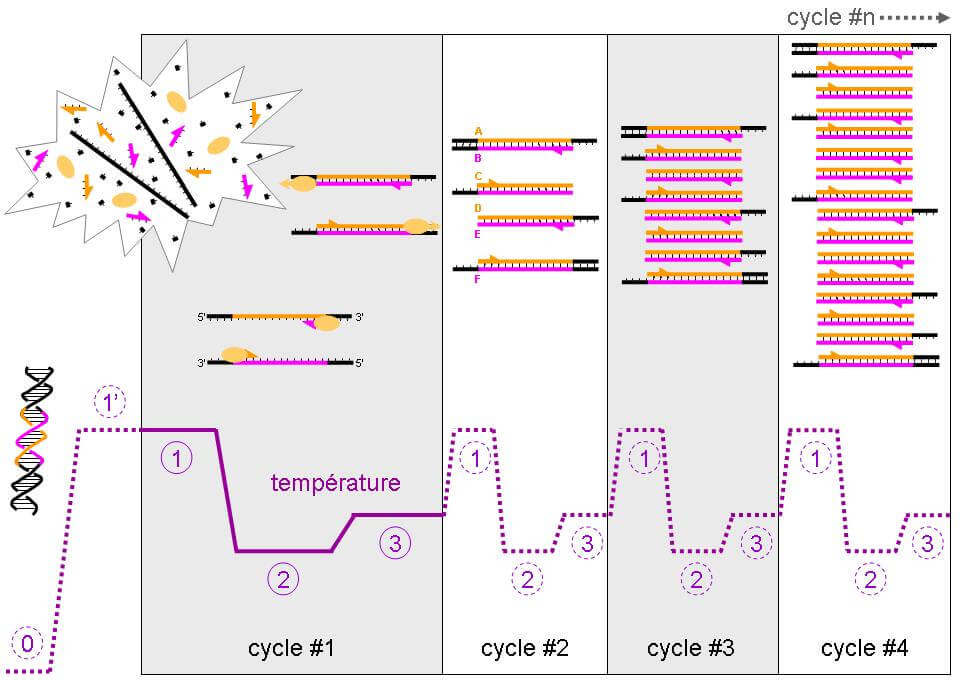
Plus cette valeur est petite, plus la synthèse des brins complémentaires aura été rapide, signifiant que le nombre d’ARN d’intérêt, à la base, était élevé et que la protéine qu’il va donner sera fortement exprimée [3].
Cette technique est également applicable pour les ARNs non codants mais ne donnera évidemment pas d’information sur le taux d’expression futur d’une protéine, car un ARN non codant ne code pour aucune protéine, comme son nom l’indique. Qui plus est, la notion d’expression d’une protéine à partir de données de transcriptomique est complexe car la traduction (ARN en protéines) peut également être régulée à la hausse ou à la baisse. La notion la plus importante est donc purement quantitative, avec un taux d’expression des ARN, reflétant l’activité génique et éventuellement la synthèse protéique.
Que fait-on des données de transcriptomique ?
Mesurer l’expression des gènes dans différents tissus, âge ou conditions physiopathologiques, comme on le fait grâce à l’étude du transcriptome, permet de mieux comprendre comment un gène donné sera régulé et donne des informations importantes concernant le fonctionnement et les besoins d’un organe donné [4]. La transcriptomique peut également être utilisée pour trouver de nouvelles fonctions à un gène et/ou découvrir de nouveaux gènes. Toutes ces applications mènent évidemment à une meilleure compréhension des maladies, de leurs fonctionnements et de leurs facteurs de risques génétiques [4]. En parallèle à ces informations, la transcriptomique permet aussi une analyse de la totalité des ARNs, comprenant les ARN codants dont nous avons parlé (ou ARN messager ou ARNm), mais également les ARNs non codants.
Les ARNs non codants : des perspectives d’avenir
Il est désormais acquis qu’environ 70% du génome est transcrit en ARN mais que seulement 2% donneront des protéines [5]. Les ARNs non codants sont donc largement majoritaires et regroupent [6]:
- les miARNs, ou micro-ARNs, des petits ARNs d’environ 20 paires de base qui ont un rôle majeur dans la régulation de l’expression génique. En effet, ils ont la possibilité de se fixer à l’ARNm, empêchant sa traduction en protéine par différent mécanismes : soit l’ARNm est détruit, soit l’ARNm est déstabilisé, soit l’ARNm va tout de même jusqu’au ribosome mais ne sera pas capable de traduire correctement la protéine.
- les ARNt, dits de transfert, dont le rôle est de lier les amino-acides aux ARNm au sein des ribosomes lors de la traduction. De ce fait, les ARNt sont nécessaires à la traduction et à la biosynthèse des protéines en accord avec la séquence génétique.
- les ARNr, ou ARN ribosomaux, contenus dans les ribosomes et dont le rôle est central dans la traduction. Ces ARNr sont parmi les plus anciens et sont extrêmement conservés entre les espèces. Ils servent très souvent de référence lors des analyses de transcriptomique.
- les siARNs, ou ARNs interférents (« small-interfering RNA »), similaires aux miARNs mais intervenant dans des voies de signalisation différentes. Ils ont un rôle important dans la régulation de la traduction car leur association avec les ARNm entraîne leur destruction (et l’absence de production de protéines). Leur forme synthétique est très largement utilisée dans l’industrie pharmaceutique et la recherche.
- les piwiARNs ou piARN (pour « piwi-interfering »), qui interagissent avec les protéines piwi, des protéines régulatrices capables de se lier à l’ARN. Lorsque les piwiARNs forment un complexe avec leur protéines cibles, ils peuvent réguler des phénomènes épigénétiques et post-transcriptionnels.
- les snoARNs (pour « Small-NucleOlar »), des petits ARNs associés aux modifications (méthylation, entre autres) des autres ARNs.
- les snARNs (pour « small nuclear »), qui aide à la synthèse des ARNm.
- les exARNs (pour « exosomal »), de petits ARNs ou portions d’ARN présents à l’extérieur des cellules dans ce qu’on appelle les exosomes (des petites vésicules).
- les lncARNs (pour « long non coding »), des ARNs non codants plus longs (environ 200 paires de bases), dont la fonction est encore débattue.
La découverte des ARNs non codants, en particulier les ARN interférents, a valu le prix Nobel de physiologie et médecine au Pr Fire et au Pr Mello en 2006. La raison de cette récompense est simple: leur découverte était cruciale à la compréhension de la régulation des ARNm, un processus relativement flou. Les miARNs et siARNs sont actuellement les plus étudiés car ils ont la capacité d’envoyer un signal de dégradation à la cellule pour détruire les ARNm qu’ils régulent. Qui plus est, ils ont été retrouvés dans le sang, ce qui en fait des biomarqueurs importants des processus biologiques et des pathologies [7].
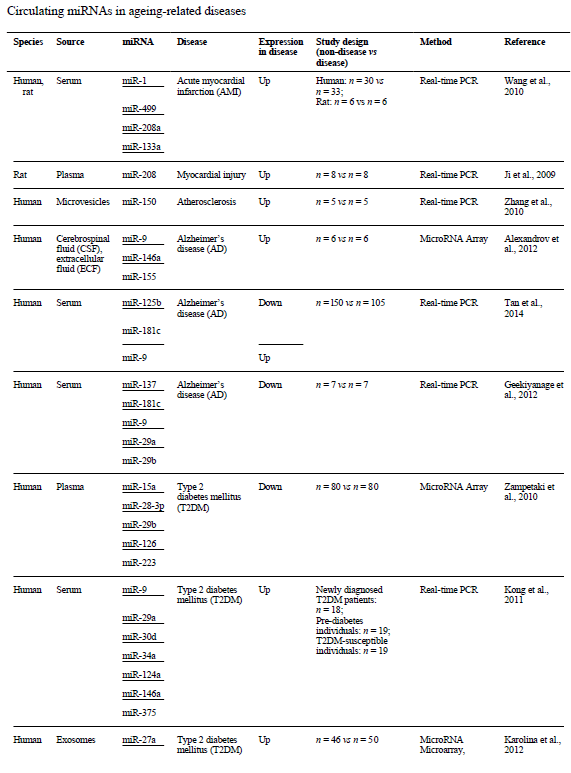
Grâce à l’avancée des techniques de transcriptomique, il est désormais possible de détecter ces petits ARNs dans le sang, dans les organes et parfois au niveau d’une seule cellule. Cela a donné lieu à une vague de publications scientifiques depuis le début des années 2000, étudiant les relations entre ARNs non codants et pathologies. Par exemple, le niveau d’expression de miR-21 est augmenté dans les maladies cardiovasculaires, celui de miR-155 est augmenté dans les situations inflammatoires, celui de miR-9 est augmenté dans la maladie d’Alzheimer, celui de miR-126 est diminué dans les diabètes ou celui de miR-150 est augmenté dans l’athérosclérose [8]. La table ci-contre résume les miARNs impliqués dans les maladies liées au vieillissement.
Ces miARNs circulants sont a priori de bons biomarqueurs de certaines maladies et conditions physiologiques. Ce sont également de nouvelles pistes pour développer des médicaments capable de réguler la synthèse protéique et peut-être participer à la guérison de ces pathologies liées à l’âge. Du fait de leur taille et de leur capacité à passer la barrière hémato-encéphalique, ce sont aussi de bons candidats thérapeutiques eux-mêmes. Dans le cancer, les miARNs et le lncARNs sont extrêmement prometteurs, avec des dérégulations importantes [9, 10]. L’injection de miR-16 chez des souris modèles du cancer de la prostate a notamment démontré la régulation à la baisse de la cible de ce miARN et une diminution de la masse tumorale [11].
La transcriptomique au service du vieillissement
Au delà du rôle des ARNs non codants en tant que biomarqueurs et cibles thérapeutiques, ce sont également des ARNs qui peuvent être régulés au cours de la vie. Par exemple, la télomérase, une enzyme qui ajoute des segments protecteurs à nos chromosomes pour éviter la perte d’information au cours des divisions cellulaires (voir dossier télomères), est ce qu’on appelle une reverse transcriptase. Ce type d’enzyme est capable de rétro-transcrire un ARN en ADN et c’est ce qu’il se passe au niveau des télomères : la télomérase est porteuse d’ARN spécifique qu’elle va ajouter au bout de nos chromosomes une fois transformé en ADN [12]. Ces ARNs non codants sont des protecteurs centraux de notre génome et leur niveau diminue avec l’âge, tout comme l’activité de la télomérase.
En parallèle, les profils transcriptomiques globaux (pas seulement les ARNs non codants) de nos cellules varient également au cours du vieillissement. Dans nos cellules immunitaires, les ARNs impliqués dans l’inhibition de l’autophagie (système de détoxification de la cellule) étaient augmentés alors que ceux impliqués dans la régulation de la phosphorylation oxydative (production d’oxydants), la synthèse du cytosquelette ou la réponse à l’insuline étaient diminués [13]. Dans le cerveau, et plus particulièrement la matière grise, les ARNm des voies de prolifération, d’adhérence et de différentiation cellulaire étaient régulés à la baisse en parallèle d’une augmentation des ARNm impliqués dans les les voies inflammatoires, suggérant une diminution des processus de régénération cellulaire et une augmentation de la neuro-inflammation avec l’âge [14, 15]. Il apparaît d’ailleurs que ces changements se produisent plus rapidement chez la femme, expliquant probablement la prévalence plus importante des maladies neurodégénératives dans ce segment de la population [16].
Des nouvelles découvertes ont lieu tous les jours et de plus en plus d’équipes s’intéressent au vieillissement en temps que tel. Une étude de 2014 s’est notamment lancée dans une étude du transcriptome sanguin de plus de 2500 personnes dans le cadre du vieillissement physiologique (sans pathologies associées). Ils ont mis en évidence que les voies d’activation des lymphocytes T, d’élongation des ARN lors de la transcription, de cytolyse et des processus métaboliques liés à l’ADN étaient tous modifiés et que ces modifications étaient associés à l’espérance de vie [17]. Chez la souris, une autre équipe de recherche s’est intéressée à la différence entre le vieillissement physiologique et le vieillissement pathologique. Ils ont ainsi prélevé régulièrement des biopsies de cinq organes, le foie, le rein, la rate, le poumon et le cerveau, tout au long de la vie des souris et étudié leur transcriptome. Au cours du temps, les chercheurs ont mis en évidence des changements liés au vieillissement, parfois accentués ou complétés par des changements liés aux pathologies qui apparaissent avec l’âge [18].
Toutes ces approches combinées offrent une vue complémentaire des données de génomique et permettent d’appréhender le vieillissement sous différents angles : à la fois implémenter les outils diagnostiques et thérapeutiques, mais aussi découvrir de nouvelles voies ou de nouveaux gènes impliqués dans les modifications de notre corps et de ses fonctions au cours de la vie.
Tout notre dossier Approches « omics »
Les approches « omics » : mieux comprendre notre vieillissement
Qu’est-ce qu’il se cache derrière les approches « omics » ? Quand on parle de génomique, transcriptomique ou protéomique, à quoi s’intéresse-t-on ? Un petit guide pour mieux comprendre !
Partie 1 : Parlons peu, parlons génomique !

Difficile de ne pas s’étendre sur la génomique et toutes ses applications. C’est la plus ancienne des approches « omics » mais c’est aussi celle qui est la plus étudiée. Elle a donné naissance au concept d’épigénétique et ouvert la porte à des espoirs jusque là impossibles !
Partie 2 : La transcriptomique, une science en constante évolution.

La découverte des ARN non codants a valu un prix Nobel, c’est dire l’importance de cette discipline. La transcriptomique c’est l’ouverture d’un champ de possibles, la découverte de nouveaux mécanismes et la compréhension progressive de la régulation de la transcription.
Partie 3 : Protéomique, un meli-melo de disciplines
 La protéomique, c’est avant tout une approche multiple, prenant en compte les interactions avec d’autres disciplines, notamment la génomique, et faisant appel à des concepts intercroisés avec l’immunologie, la fonction cellulaire ou la nutrition.
La protéomique, c’est avant tout une approche multiple, prenant en compte les interactions avec d’autres disciplines, notamment la génomique, et faisant appel à des concepts intercroisés avec l’immunologie, la fonction cellulaire ou la nutrition.
Partie 4 : La métabolomique, la dernière-née des « omics »
 « Last but not least » comme diraient nos amis anglophones. La métobolomique, c’est la compréhension de réseaux de régulation complexes et la découverte quotidienne de nouveaux acteurs dans les communications entre nos cellules.
« Last but not least » comme diraient nos amis anglophones. La métobolomique, c’est la compréhension de réseaux de régulation complexes et la découverte quotidienne de nouveaux acteurs dans les communications entre nos cellules.
Références :
[1] Wang Z, Gerstein M, Snyder M, RNA-Seq: a revolutionary tool for transcriptomics. Nat Rev Genet. 2009; 10(1):57-63
[2] Schena M, Shalon D, Davis RW, Brown PO, Quantitative monitoring of gene expression patterns with a complementary DNA microarray. Science. 1995; 270(5235):467-70
[3] Alwine JC, Kemp DJ, Stark GR, Method for detection of specific RNAs in agarose gels by transfer to diazobenzyloxymethyl-paper and hybridization with DNA probes. Proc Natl Acad Sci U S A. 1977; 74(12):5350-4
[4] Han Y, Gao S, Muegge K, Zhang W, Zhou B. Advanced Applications of RNA Sequencing and Challenges. Bioinformatics and Biology Insights. 2015;9(Suppl 1):29-46
[5] Bertone P, Stolc V, Royce TE, Rozowsky JS, Urban AE, Zhu X, Rinn JL, Tongprasit W, Samanta M, Weissman S, Gerstein M, Snyder M, Global identification of human transcribed sequences with genome tiling arrays. Science. 2004; 306(5705):2242-6
[6] Hirose T, Mishima Y, Tomari Y. Elements and machinery of non-coding RNAs: toward their taxonomy. EMBO Reports. 2014;15(5):489-507
[7] Ling H, Fabbri M, Calin GA. MicroRNAs and other non-coding RNAs as targets for anticancer drug development. Nature reviews Drug discovery. 2013;12(11):847-865
[8] Jung HJ, Suh Y. Circulating miRNAs in Ageing and Ageing-Related Diseases. Journal of genetics and genomics. 2014;41(9):465-472
[9] Gutschner T, Diederichs S. The hallmarks of cancer: A long non-coding RNA point of view. RNA Biology. 2012;9(6):703-719
[10] Berindan-Neagoe I, Monroig P, Pasculli B, Calin GA. MicroRNAome genome: a treasure for cancer diagnosis and therapy. CA: a cancer journal for clinicians. 2014;64(5):311-336
[11] Iguchi H, Kosaka N, Ochiya T, Secretory microRNAs as a versatile communication tool. Commun Integr Biol. 2010; 3(5):478-81
[12] Ly H, Blackburn EH, Parslow TG. Comprehensive Structure-Function Analysis of the Core Domain of Human Telomerase RNA. Molecular and Cellular Biology. 2003;23(19):6849-6856
[13] Reynolds LM, Ding J, Taylor JR, et al. Transcriptomic profiles of aging in purified human immune cells. BMC Genomics. 2015;16(1):333
[14] Kochunov P, Charlesworth J, Winkler A, et al. Transcriptomics of cortical gray matter thickness decline during normal aging. NeuroImage. 2013;0:273-283
[15] Kang HJ, Kawasawa YI, Cheng F, et al. Spatiotemporal transcriptome of the human brain. Nature. 2011;478(7370):483-489
[16] Yuan Y, Chen Y-PP, Boyd-Kirkup J, Khaitovich P, Somel M. Accelerated aging-related transcriptome changes in the female prefrontal cortex. Aging Cell. 2012;11(5):894-901
[17] Van den Akker EB, Passtoors WM, Jansen R, et al. Meta-analysis on blood transcriptomic studies identifies consistently coexpressed protein–protein interaction modules as robust markers of human aging. Aging Cell. 2014;13(2):216-225
[18] Melis JPM, Jonker MJ, Vijg J, Hoeijmakers JHJ, Breit TM, van Steeg H. Aging on a different scale – chronological versus pathology-related aging. Aging (Albany NY). 2013;5(10):782-788
Dr. Marion Tible

Author/Reviewer
Auteure/Relectrice
Marion Tible has a PhD in cellular biology and physiopathology. Formerly a researcher in thematics varying from cardiology to neurodegenerative diseases, she is now part of Long Long Life team and is involved in scientific writing and anti-aging research.
More about the Long Long Life team
Marion Tible est docteur en biologie cellulaire et physiopathologie. Ancienne chercheuse dans des thématiques oscillant de la cardiologie aux maladies neurodégénératives, elle est aujourd’hui impliquée au sein de Long Long Life pour la rédaction scientifique et la recherche contre le vieillissement.
En savoir plus sur l’équipe de Long Long Life
Dr Guilhem Velvé Casquillas

Author/Reviewer
Auteur/Relecteur
Physics PhD, CEO NBIC Valley, CEO Long Long Life, CEO Elvesys Microfluidic Innovation Center
More about the Long Long Life team
Docteur en physique, CEO NBIC Valley, CEO Long Long Life, CEO Elvesys Microfluidic Innovation Center
En savoir plus sur l’équipe de Long Long Life